Nature Methods:新算法利用空间转录组数据构建肿瘤的“空间进化图谱”
时间:2024-11-17 12:00:47 热度:37.1℃ 作者:网络
癌症的进展由体细胞突变和染色质重塑共同驱动,包括核苷酸变异(SNV)、体细胞拷贝数变异(CNA)和大规模结构变异等。对批量肿瘤或分离单细胞中的体细胞突变进行测序可揭示肿瘤内部的遗传异质性,并能重建肿瘤的进化史;肿瘤之间也表现出异质性,并能够在物理空间内发生进展。分析肿瘤在时间和空间上的体细胞进化是癌症研究中的一个关键挑战,常因缺乏空间数据而受阻。
近年来,空间测序技术的发展为肿瘤时空演化研究提供了一个有前景的方法,但这类技术仍处于积极发展阶段,尚未得到广泛应用。目前,空间转录组学(SRT)技术能够同时测量肿瘤组织中数千个空间位置的基因表达,但无法直接揭示肿瘤中的基因组突变,特别是CNA这一类关键的基因组变化。
近期,美国普林斯顿大学和华盛顿大学的科研团队合作在Nature Methods发表了题为“Inferring allele-specific copy number aberrations and tumor phylogeography from spatially resolved transcriptomics”的文章。研究团队介绍了一种名为“CalicoST”的算法,可从SRT数据中推断等位基因特异性CNAs,并利用这些CNAs来重建肿瘤的空间进化轨迹或“系统地理学图谱”。CalicoST能够识别能够识别重要CNA类别,包括拷贝中性杂合性缺失(CNLOH)和镜像亚克隆CNAs,表征等位基因特异性CNAs以及肿瘤克隆随时间的积累在物理空间中的扩散。经验证,CalicoST可达到至少86%的准确率,相较先前方法高21%。总之,CalicoST可以用于研究肿瘤的空间演变、进展和转移,并有助于进一步应用于肿瘤的诊断和治疗。

文章发表在Nature Methods
主要研究内容
01 CalicoST算法概述
CalicoST可从肿瘤的一个或多个SRT样本中推断等位基因特异性CNA并重建肿瘤进化的系统地理学图谱。CalicoST具有以下主要特征:1、识别每个肿瘤克隆转录区域的等位基因特异性的整数拷贝数,揭示总拷贝数分析不可见的事件,如CNLOH和镜像亚克隆CNAs;2、随后为每个spot分配一个克隆标记,标明该spot的等位基因特异性拷贝数谱;3、推断出与已识别的拷贝数谱(肿瘤克隆)相关的系统发育,以及结合体细胞进化和克隆空间演化的系统地理学图谱;4、 利用非单细胞分辨率的SRT技术(如10x Genomics Visium)推断并模拟正常细胞混合物,以推断更准确的等位基因特异性拷贝数和肿瘤克隆;5、同时分析来自同一肿瘤的多个区域或对齐的SRT切片。
总之,CalicoST重建了一个系统地理学图谱来表征推断出的克隆之间的祖先关系以及这些克隆祖先的空间位置。CalicoST使用LOH事件推断癌症克隆的系统发育,LOH事件具有不可逆的重要特性,最终从一个或多个肿瘤SRT样本中推断出等位基因特异性CNAs和肿瘤的空间演化。
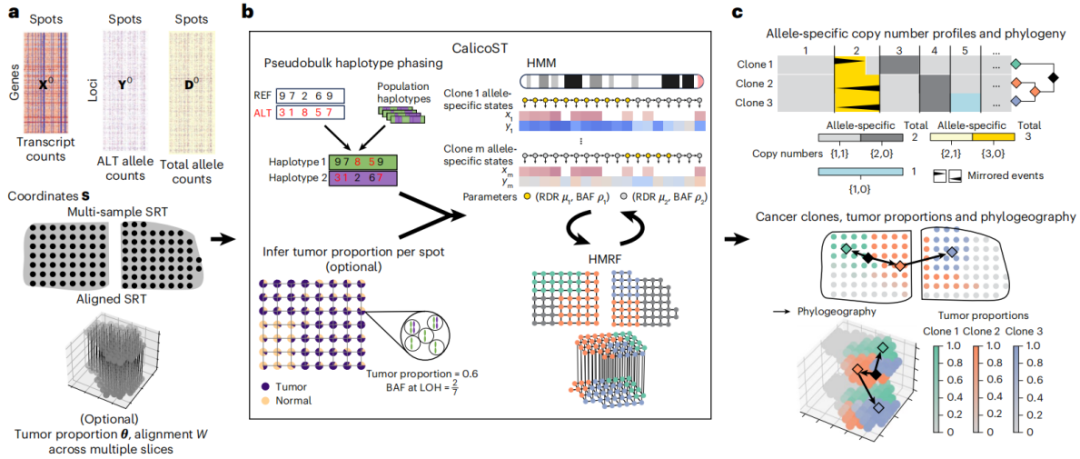
图1. CalicoST工作流程及概述
02 CalicoST可准确推断等位基因特异性CNA
研究团队使用华盛顿大学队列(HTAN)中12名患者(26个切片)的10x Genomics Visium Spatial Transcriptomics数据对CalicoST进行验证。结果显示,在具有足够肿瘤纯度且有匹配全外显子测序(WES)数据的9位患者中,CalicoST推断的等位基因CNV平均准确率为86%,比先前方法高出21%;在预测拷贝数异常的基因组bins时,平均准确率为95%,平均召回率为90%。
通过对HTAN中两名胰腺导管腺癌患者的SRT数据进行分析,研究团队评估了CalicoST在正常细胞混合度高(肿瘤细胞度低)和空间组织复杂的肿瘤中推断CNA和癌症克隆的能力。结果显示,CalicoST确定了多个癌症克隆,其中LOH区域在BAF中表现出明显差异。此外,CalicoST 还揭示了批量WES数据中遗漏的肿瘤异质性和克隆特异性拷贝数改变。
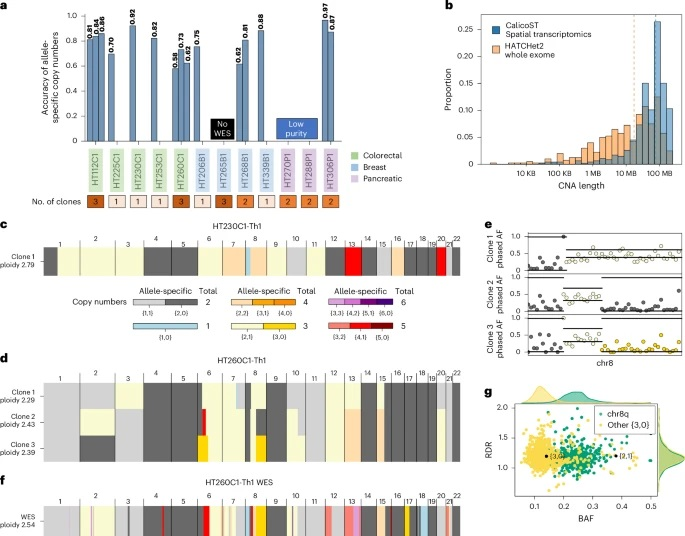
图2.CalicoST推断HTAN样本中准确的等位基因特异性拷贝数
03 CalicoST具有较高的精度和空间相关性
研究团队将CalicoST与现有的从单细胞转录组测序(scRNA-seq)数据和空间转录组学中鉴定CNAs的方法(Numbat、STARCH和inferCNV)进行比较,以评估CalicoST推断CNAs和肿瘤克隆空间分布的准确性。结果显示,聚焦于具有最多CNA事件的4个结直肠癌(CRC)肝转移样本,CalicoST在所有样本中的准确性均最高,在推断等位基因特异性拷贝数方面优于Numbat(平均准确率高出25%),在推断总拷贝数方面优于STARCH(平均准确率高出59%)和interCNV(平均准确率高出90%)。
此外,在两个CRC肝转移患者样本中,CalicoST推断的肿瘤克隆空间分布比Numbat和interCNV更具一致性。相比之下,Numbat识别的肿瘤克隆具有较低的空间相关性。
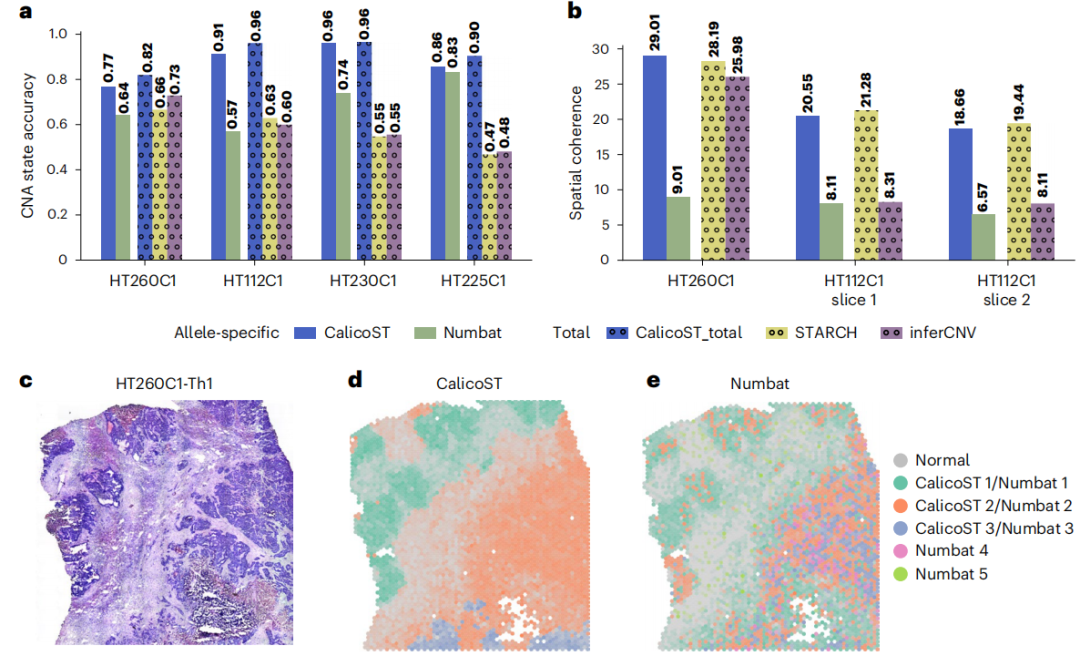
图3. CalicoST和其他CNAs推断方法的性能比较
04 CalicoST在三维空间推断肿瘤的演化
接下来,研究团队使用CalicoST在三维空间中为HTAN队列一名CRC患者和一名乳腺癌患者构建肿瘤克隆系统进化树,这两名患者具有多个相邻的10x Genomics Visium空间转录组学数据切片。对于CRC肝转移患者,CalicoST在三维肿瘤组织中鉴定了三个空间上一致的克隆,并基于这些克隆中的CNAs推断出系统进化树。该系统进化树显示了肿瘤的扩展,从祖先克隆1(橙色)分支到两侧的两个克隆(绿色和蓝色),这三个克隆具有不同的等位基因特异性拷贝数谱。
在乳腺癌患者中,CalicoST在五个切片中鉴定了两个肿瘤克隆,这些克隆在三维空间中对齐,并重建了两个克隆之间的系统地理学图谱。结果显示,祖先(黑色)克隆位于两个克隆之间,与克隆2的物理距离较近。该肿瘤的空间演化在Z轴方向上分量较强,这显示了三维系统地理图谱重建的优势。
此外,研究团队还通过分析乳腺癌患者空间距离大于200 μm的两个切片,评估了CalicoST在空间间隔较大的肿瘤切片上的准确性。结果显示,CalicoST推断出的肿瘤克隆与基于5个切片推断出的克隆基本一致。CalicoST在两个切片上推断的等位基因特异性拷贝数谱与通过WES数据推断的基因组CNAs相匹配,分别为79.2%和68.0%。这一结果表明CalicoST可以用于分析来自远距离切片的三维肿瘤克隆。
图4. CalicoST推断的三维肿瘤演化结果
最后,研究团队将 CalicoST 应用于一名前列腺癌患者癌变前列腺横切面的5个SRT切片中,推断出等位基因特异性CNAs和系统地理学图谱。CalicoST发现了5个癌症克隆,其具有不同的拷贝数谱;推断出的癌症克隆空间分布与病理学家标注的肿瘤区域在视觉上一致。此外,重建的系统地理学图谱显示,前列腺横截面左右两侧存在镜像亚克隆CNA,这表明肿瘤发生了趋同进化,揭示了克隆在物理和遗传空间上的分离。
结 语
综上所述,该研究报道了CalicoST算法,该算法能够推断等位基因特异性拷贝数变异,并利用SRT数据在时间和空间上重建与肿瘤克隆相关的系统地理学图谱。CalicoST使用推断的杂合性缺失(LOH)事件来构建与肿瘤克隆和空间系统地理相关的系统发育,将肿瘤的基因组和空间演化整合到一个统一的模型中;当多个切片可用时,CalicoST还能够推断出跨切片的系统进化树,包括空间肿瘤进化的三维模型。CalicoST可为肿瘤的拷贝数驱动因素、肿瘤的空间异质性和空间进化提供有价值的见解,为整合遗传进化、表观遗传变化和细胞类型的空间组织的其他生物学分析提供基础。
参考原文:
Ma, C., Balaban, M., Liu, J. et al. Inferring allele-specific copy number aberrations and tumor phylogeography from spatially resolved transcriptomics. Nat Methods (2024).
https://www.nature.com/articles/s41592-024-02438-9


